PacBio의 highly accurate long-read sequencing (HiFi)을 활용하여
고해상도로 미생물의 게놈을 분석할 수 있습니다.
UNDERSTAND THE EVOLVING PANDEMIC WITH PACBIO SEQUENCING
새로운 변종의 확산으로 whole genome sequencing이 SARS-CoV-2에 대한 대응의 중요한 부분으로 되었습니다. 이 새로운 전염병 단계에서 PacBio는 바이러스 감시를 강화하기 위해 미국 정부, 학계 및 기업 연구소를 지원하기 위해 최선을 다하고 있습니다.
Targeted Sequencing for SARS-CoV-2 Surveillance
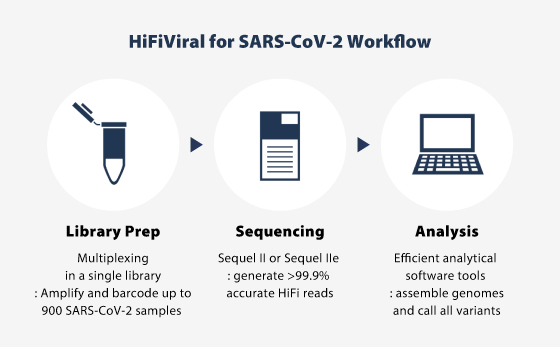
Sequel IIe 시스템의 HiFi read는 SARS-CoV-2를 빠르고 쉽게 시퀀싱 할 수 있는 안정적이고 비용면에서도 효율적인 high-throughput solution을 제공합니다.
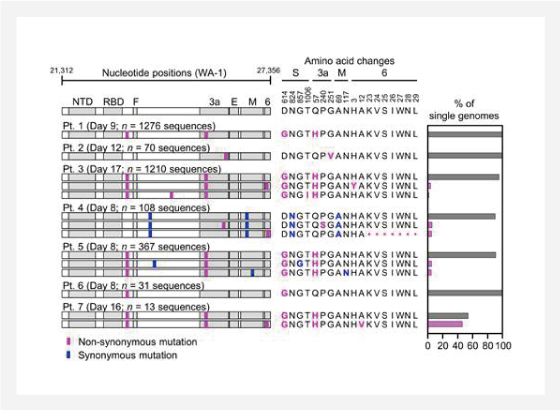
COVID-19의 사례 중에 발견되는 SARS-CoV-2의 돌연변이 서열은 이론적으로 주로 발견되는 바이러스의 서열을 타겟으로 하는 항 바이러스 요법 또는 면역 반응을 바이러스가 회피 할 수 있게 합니다. 그러나 일반적으로 사용되는 시퀀싱 기술은 각 샘플 내에서 변종 바이러스 서열을 탐지하도록 설계되지 않았습니다. 이 문제를 해결하기 위해 연구팀은 바이러스 표면 단백질을 인코딩하는 영역에 걸쳐 많은 수의 개별 SARS-CoV-2 게놈 RNA 분자를 시퀀싱하는 새로운 기술을 개발했습니다.
이전에 일반적으로 사용되는 SARS-CoV-2의 sequencing/analysis과정에서는 하나의 consensus sequence밖에 검출할 수 없었지만 RNA RT과정에서 UMI를 이용하고 PacBio long read target sequencing (target size=5.8kb)을 통해 각 sample에서 virus spike의 mutation을 반영한 multiple sequence의 variant (virus diversity)를 검출하는 방법을 발표하였습니다.
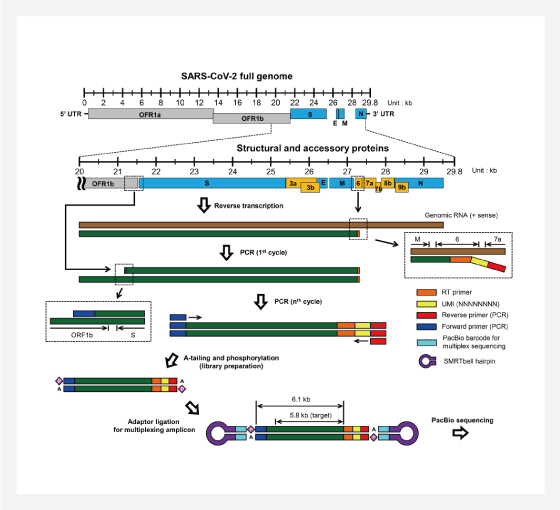
샘플에서부터 HT-SGS (high-throughput single-genome amplification and sequencing)의 과정
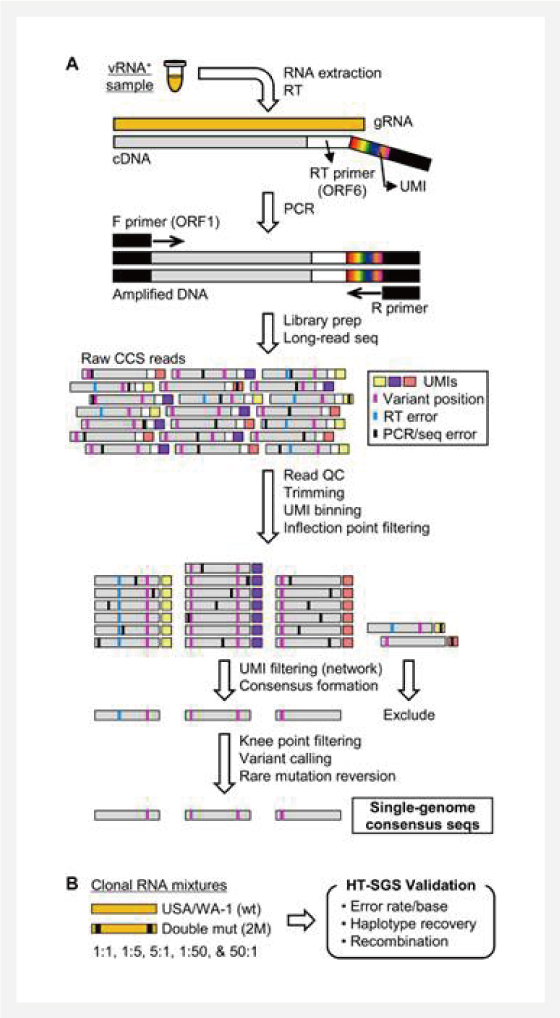
A. Overview of HT-SGS data generation and analysis.
B. data 생성 및 분석의 검증과정을 위해 clonal RNA 역전사체의 USA/WA-1와 double mutant sequences로부터 in vitro에서 1:1, 1:5, 5:1, 1:50, 50:1의 비율로 섞어 해당 방법을 통해 그 비율대로 검출되는지를 검증
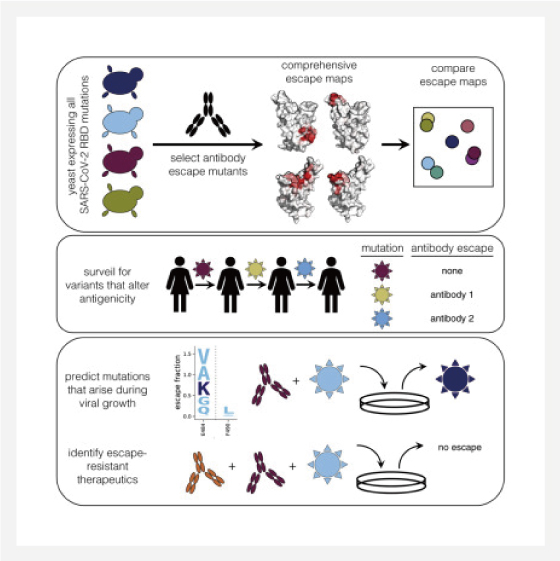
Highlights • Develop system to map all SARS-CoV-2 RBD mutations that escape antibody binding • Escape maps inform surveillance for possible antigenic evolution• Escape maps predict which mutations emerge when virus grown in presence of antibody |
HiFi Reads Offer the Benefits of Short Reads and Long Reads in One Easy-to-Use Technology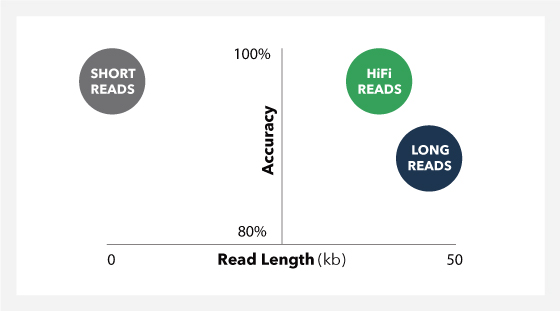
HiFi read는 모든 변이 유형을 감지할 수 있는 높은 정확도 (> 99.9 %)와 가장 복잡한 유전체와 전체 전사체를 assemble하는데 필요한 충분히 긴 길이(최대 25kb)를 제공합니다.